


Caso ocorrido em 2019 foi investigado por equipe multicêntrica, que revelou se tratar de um subtipo do patógeno causador da doença de Newcastle. Segundo os pesquisadores, o risco para humanos e aves domésticas, como galinhas, é baixo (foto: acervo dos pesquisadores)
Caso ocorrido em 2019 foi investigado por equipe multicêntrica, que revelou se tratar de um subtipo do patógeno causador da doença de Newcastle. Segundo os pesquisadores, o risco para humanos e aves domésticas, como galinhas, é baixo
Caso ocorrido em 2019 foi investigado por equipe multicêntrica, que revelou se tratar de um subtipo do patógeno causador da doença de Newcastle. Segundo os pesquisadores, o risco para humanos e aves domésticas, como galinhas, é baixo
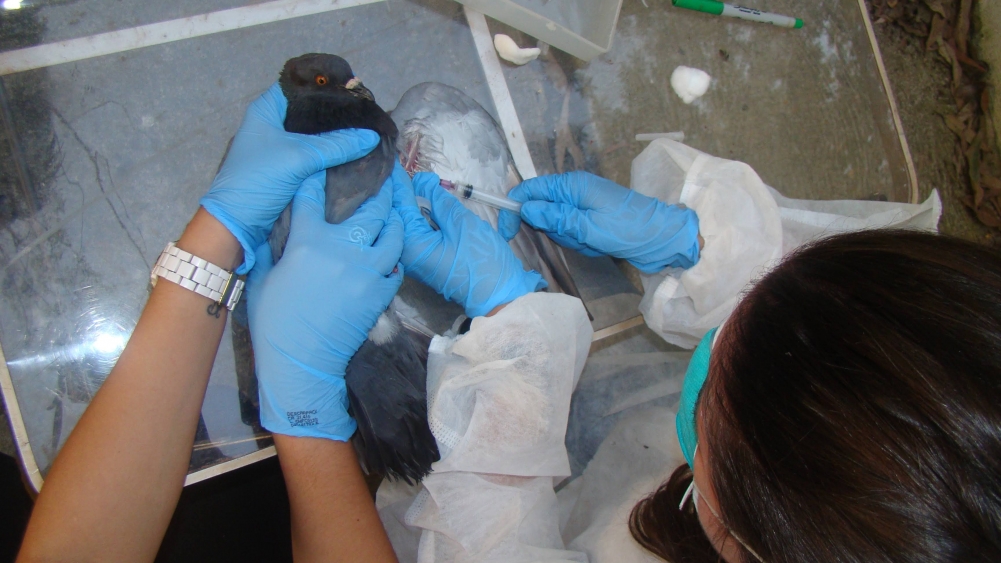
Caso ocorrido em 2019 foi investigado por equipe multicêntrica, que revelou se tratar de um subtipo do patógeno causador da doença de Newcastle. Segundo os pesquisadores, o risco para humanos e aves domésticas, como galinhas, é baixo (foto: acervo dos pesquisadores)
Maria Fernanda Ziegler | Agência FAPESP – Em 2019, dias antes do evento climático que transformou o dia em noite na cidade de São Paulo, dezenas de pombos começaram a cair mortos misteriosamente. Os animais apresentavam alguns ferimentos, sintomas neurológicos e foram encontrados já sem vida ou moribundos próximos ao Centro de Controle de Zoonoses da capital paulista.
Uma equipe multicêntrica de pesquisadores descobriu que, apesar da proximidade das datas, as mortes não estavam relacionadas com a poluição gerada pelas queimadas na Amazônia. Eram, na verdade, efeito de um paramixovírus aviário do tipo 1 – também conhecido como vírus da doença de Newcastle –, com um genótipo denominado VI.2.1.2, que costuma ser letal para pombos. Também conhecido como paramixovírus de pombo (PPMV), esse patógeno raramente infecta pessoas e, quando isso ocorre, é por meio do contato próximo com animais doentes.
“Descobrimos se tratar de um vírus que circulava silenciosamente no Brasil desde 2014. Com base nos dados moleculares, notamos ser o mesmo PPMV que havia sido identificado em Porto Alegre [RS] cinco anos antes. E são cerca de 1.100 quilômetros de distância entre as duas cidades. Tal fato demonstra o potencial desse patógeno de se disseminar sem ser percebido”, afirma Luciano Matsumiya Thomazelli, pesquisador do Laboratório de Virologia Clínica e Molecular do Instituto de Ciências Biomédicas da Universidade de São Paulo (ICB-USP) e primeiro autor do artigo, publicado na revista Viruses.
Desde 2005, o laboratório conta com uma equipe que vai a campo para fazer pesquisa de vigilância epidemiológica em diferentes regiões do Brasil. A atividade é conduzida no âmbito da Rede de Diversidade Genética de Vírus (VGDN), financiada pela FAPESP e coordenada pelo professor da USP Edison Luiz Durigon.
Atualmente, o grupo integra a Rede Nacional de Vigilância de Vírus em Animais Silvestres (PREVIR), fomentada pelo Ministério da Ciência, Tecnologia e Inovações (MCTI) por meio do Conselho Nacional de Desenvolvimento Científico e Tecnológico (CNPq).
Mata pombos
O vírus da doença de Newcastle normalmente causa doença em galinhas, mas não em pombos. Segundo os pesquisadores, porém, com o genótipo VI.2.1.2 ocorre justamente o contrário.
“Ele é endêmico na população de pombos no mundo inteiro, causando sintomas neurológicos e alta mortalidade. Há relatos frequentes de casos na Ásia, na Europa e na América do Norte. Apesar de este ser o segundo registro no Brasil, não é caso para alarde, pois esse genótipo não representa um grande risco para humanos ou para a avicultura”, avalia Helena Ferreira, professora da Faculdade de Zootecnia e Engenharia de Alimentos da USP em Pirassununga, integrante da rede PREVIR-MCTI e coordenadora da pesquisa.
Como ressaltam os cientistas, o monitoramento zoonótico tem se mostrado de extrema importância para o controle de epidemias, surtos e para alertar sobre a emergência de novas doenças.
“É fundamental uma vigilância ostensiva e ativa em todo o país para identificar e controlar as populações de pombos não só perto das granjas, mas também nas áreas urbanas. O monitoramento do vírus da doença de Newcastle é importante até mesmo do ponto de vista econômico, já que o Brasil é o maior exportador de carne de frango do mundo”, diz Thomazelli.
Trabalho de equipe
Para desvendar a doença misteriosa que acometia pombos na capital, foi necessário acionar uma ampla rede de pesquisadores. Primeiro o Centro de Vigilância e Zoonoses do Estado de São Paulo identificou a morte das aves e acionou o Serviço Veterinário Oficial.
“De início imaginou-se que a causa pudesse ser uma bactéria, mas não se identificou nenhuma espécie patogênica. Enviaram amostras para o ICB-USP e para o Laboratório Federal de Defesa Agropecuária. Lá eles fizeram a caracterização, que é o padrão recomendado para vírus de notificação obrigatória, pois afetam aves domésticas. Coube ao nosso laboratório em Pirassununga realizar a análise do genoma viral”, conta Ferreira.
A pesquisadora também realizou análises para a identificação de lesões no tecido. “Fizemos o sequenciamento do genoma completo desse vírus, que identificamos como VI.2.1.2. Isso nos permite fazer uma investigação mais aprofundada, comparar com surtos em outras partes do mundo e também acompanhar a evolução do patógeno aqui no país. Esse conhecimento nos ajuda a prever como o vírus vai se comportar daqui para a frente. Se pode se adaptar a outras aves silvestres, por exemplo”, diz.
Segundo a pesquisadora, a análise genômica mostrou que o vírus encontrado em São Paulo e no Rio Grande do Sul (em 2014) se agrupa com amostras da África.
“Outros casos precisam ser identificados para conseguirmos propor a classificação do genótipo que tem circulado no Brasil, que é relativamente diferente do africano. É muito importante fazer esse tipo de monitoramento. Nesse caso específico, esse genótipo não consegue infectar as aves domésticas [galinhas] de forma eficiente e, quando infecta, a galinha não transmite o vírus para outras com as quais convive. Existem estudos, porém, sugerindo que esse genótipo pode se adaptar em galinhas após algumas passagens e causar doença em aves domésticas também. Mesmo assim, ele não é considerado muito perigoso para as aves comerciais”, completa.
A investigação recebeu financiamento da FAPESP por meio de dois projetos (17/01125-2 e 19/13198-0).
O artigo An Outbreak in Pigeons Caused by the Subgenotype VI.2.1.2 of Newcastle Disease Virus in Brazil pode ser lido em: www.mdpi.com/1999-4915/13/12/2446/htm.
Republicar
A Agência FAPESP licencia notícias via Creative Commons (CC-BY-NC-ND) para que possam ser republicadas gratuitamente e de forma simples por outros veículos digitais ou impressos. A Agência FAPESP deve ser creditada como a fonte do conteúdo que está sendo republicado e o nome do repórter (quando houver) deve ser atribuído. O uso do botão HMTL abaixo permite o atendimento a essas normas, detalhadas na Política de Republicação Digital FAPESP.





